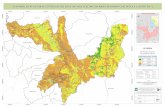
Determinación de suceptibilidad a movimientos de ladera en la provincia de Jaén, Cajamarca.
suceptibilidad jornadad
description
Transcript of suceptibilidad jornadad

Suceptibilidad por técnicas de amplificación de ácidos nucleicos

Lesiones tuberculosis > 108 bacilos
RIF 1 por cada 107-108 bacilos (100 000 000)
INH 1 por cada 105-106 bacilos (100 000)
SM 1 por cada 105-106 bacilos (100 000)
EMB 1 por cada 105-106 bacilos? (100 000)
Quinolonas 1 por cada 105-106 bacilos? (100 000)
Otro fármacos 1 por cada 105-106 bacilos ? (100 000)
PZ 1 por cada 102-103 bacilos (1 000)
Resistencia tuberculosis

Alteraciones genéticas puntuales en los genes del cromosoma bacteriano que codifican la diana del fármaco o enzimas implicadas en su activación.
No se a reportado elementos genéticos móviles (no hay transmisión horizontal de genes de resistencia es decir por procesos de conjugación, transformación, y transducción
Mutaciones espontaneas
MDR-XDR: acumulación secuencial de mutaciones en diferentes genes.
Resistencia adquirida en MTBC
4,411,529 pb

Fármaco involucrado Gen Mecanismos de acción de la del fármaco Frecuencia de mutaciones
Rifampiciana rpoB (falta de interacción de la rifampicina con la subunidad β del RNA polimerasa
Inhibición de la transcripción de genes por interacción con la subunidad β de la ARN polimerasa
96-98%
Isoniazida katG (catalasa-peroxidasa impide la activación de isoniazida)inhA (enol ACP reductasa) las mutaciones inducen la sobreexpresión del gen superando el poder inhibitorio de INH
Inhibición de la síntesis de ácidos micólicos
50-68% katG
21-34% inhA
Pirazinamida pncA (enzima pirazinamidasa) disminución de ácido pirazinoico, metabolito activo
No conocido 72-92%
Estreptomicina Amikacina
CapriomicinaKanamicina
rrs (Subunidad ribosomal 16S)rpsl (Subunidad ribosomal 12s)Impiden interacción con estreptomicina.
Inhibición de la síntesis de proteínas
8-21% rrs 64-67% rpsl
69-75%73-87%
Genes, función y mutaciones

Fármaco involucrado
Gen Mecanismo de acción del fármaco
Frecuencia de mutaciones
Etambutol embB ( enzimas aribinosiltransferasa)
sobreexpresión de este gen permite la síntesis de (arabinos galactanos)
Inhibición de componentes de la pared celular (arabino galactanos)
47-65%
Fluorquinolonas Levofloxacino, moxifloxacino
gyrA (disminución interacción fármaco con sub unidad β de
la topoisomerasa II)
Inhibición de rotura de cadenas de DNA, enrollamiento y
desenrrollamiento.
74-89%

• Detecta MTB y resistencia a RIF
• Es una hemisted Real time PCR para amplificar la secuencia del gen rpoB (189 pb) y la región 16S(209 pb)
• Integra los procesos sobre la muestra y el PCR dentro del cartucho de plástico.
• Lisis de bacteria (sonicación)• Extracción de DNA• Amplificación de DNA• Detección del amplicón
• El resultado se obtiene en un periodo de 2 horas
GeneXpert MTB/RIF

Identificación del amplicón
Utiliza tres pares de primers específicos, un par para la región 16S y dos pares para la región rpoB.El amplicón es identificado por medio de 5 sondas moleculares de desplazamiento de longitud de onda (A,B,C,D y E).
Ventajas: Equipo totalmente automatizado, mínima intervención del operador , rápido.Desventajas: Método costoso solo identifica resistencia a un solo antibiótico

MTBDR plus• Se basa en la tecnología DNA Strip• Identifica monoresistencia a INH y
RIF• Multidrogorresistente: Resistencia
INH a RIF• El análisis del gen rpoB la
resistencia a RIF• Analiza dos genes katG y inhA que
confieren resistencia a INH• El kit se puede realizar para cepas
aisladas del complejo MTB o muestras pulmonares (muestras procesadas por método de Petroff)
MTBDR sl• Identificación de resistencia a
Fluoroquinolonas (ofloxacino, levofloxacino y moxifloxacino), gen gyrA.
• Identificación de resistencia a aminoglucósidos (kanamicina, Capriomicina y Amikacina), gen rrs.
• Extremadamente drogorresistente
GenoType ®

GenoType®
ExtracciónAmplificaciónHibridación

Gen rpoB (Rifampicina)
rpoB WT1 (505-509)
rpoB WT2 (510-513)
rpoB WT3 (513-517) rpoB MUT1 D516V
rpoB WT4 (516-519)
rpoB WT5 (518-522)
rpoB WT6 (522-526) rpoB MUT2A H526YrpoB MUT2B H526DrpoB WT7 (525-529)
rpoB WT8 (529- 533) rpoB MUT3 S531L
GenoType MTBDR plus
Isoniazida
katG inhA
WT1 315 inhA WT1 -15 & -16
MUT1
S315T1
inhA WT2 -8
MUT2
S315T2
inhA MUT1 C-15T
inhA MUT2 A-16G
inhA MUT3A
T8C
inhA MUT3B
T8A

GGC ACC AGC CAG CTG AGC CAA TTC ATG CAC CAG AAC AAC CCC CTG TCC GGG TTG ACC CAC AAG CGC CGA CTG TCG GCG CTG
GlY Thr Ser Gln Leu Ser Gln Phe Met Asp Gln Asn Asn Pro Leu Ser Gly Leu Thr His Lys Arg Arg Leu Ser Ala Leu
GGC ACC AGC CAG CTG AGC CAA TTC ATG CAC CAG AAC AAC CCC CTG TCC GGG TTG ACC CAC AAG CGC CGA CTG TCG GCG CTG
507 508 509 HisCAT
ProCCG
ThrACC
LeuCTA
514 IleATA
ValCTC
517 518 519 520 MetATG
LeuTTG
523 524 525 TyrTAC
527 528 529 530 LeuTTG
532 ProCCG
510 ARGCGG
ArgCGC
LysAAA
515 TyrTAC
521 522 AspGAC
TrpTGG
533
511 512 ProCCA
GluGAG
ARGCGC
CysTGT
513 GlyGGC
LeuCTC
GlnCAG
516 ProCCC
531
GluCAA
AsnAAC
GlnCAG
rpoB WT1 rpoB WT3
rpoB WT2 rpoB WT4 rpoB WT6
rpoB WT8rpoB WT7rpoB WT5
rpoB MUT1
rpoB MUT2A
rpoB MUT2BrpoB MUT3
Gen rpoB

Gen katG y inhA
katG gene Catalasa-Peroxidasa
1
735
315
KatG codón 315AGC->ACC (Ser->Thr)AGC->ACA (Ser->Thr)
inhA (enol ACP reductasa) MabA (3-ketoacyl-ACP Reductasa)
A-16 C-15 T-8
inhA MUT1C-15-TinhA MUTA-16G
inhA MUT3A T-8CinhA MUT3B T-8A

GenoType MTBDR sl
Gen gyrA
gyrA WT1 85-90
gyrA WT2 89-93
gyrA MUT1 A90VgyrA MUT2 S91P
gyrA WT3 92-97
gyrA MUT3A D94AgyrA MUT3B D94N ó YgyrA MUT3C D94GgyrA MUT3D D94H
Gen embB
306 Met→Val (ATG→GTG)
embB MUT1B
306 Met→Ile (ATG→ATC) embB MUT1B
306 Met→lle (ATG→ATA) embB MUT1A
Gen rrs
rrs WT1 1401-1402
rrs MUT1 A1401Grrs MUT1 C1402T
rrs WT2 1484 rrs MUT2 G1484T

CAC CCG CAC GGC GAC GCG TCG ATC TAC GAC AGC CTG
85 86 87 88 89 90 91 92 93 94 95 99H P H G D A S I Y D S L
TGCC
GTGV
CCGP
GCCA
ACCT
AACNTACYGGCGCACH
gyrA WT1
gyrA WT2
gyrA WT3
gyrA MUT1
gyrA MUT2gyrA MUT3A
gyrA MUT3B
gyrA MUT 3C
gyrA MUT3D
Gen gyrB

Gen rrs
1484
rrs WT2
rrs MUT2
rrs MUT1
rrs WT1

GenoType MTBDR plus
STR; 6.35%
RIF; 15.87%
INH; 7.94%
STR+ INH; 4.76%
STR+ INH + EMB; 4.76%RIF + INH; 28.57%
RIF + INH + STR; 22.23%
RIF + INH + EMB; 4.76%XDR ; 4.76%
63 cepas aisladas resistentes de 356 aislados
Aislados MDR= 60.32%Aislados No MDR=37.78%
Fuente: Laboratorio de Microbiología Clínica, INER, 2014

GenoType MTBDR plus
Resistencia en rpoB; 97.36%
Resistencias no detec-tadas ; 2.64%
Sensibilidad de RIF en 38 aislado MDR
37/38 aislados
Mtb no identi-ficadas; 40.00%
Resistente a rpoB; 60.00%
10 cepas monorresistentes a
rifampicina Fuente: Laboratorio de Microbiología Clínica, INER, 2014
6/10 aislados
4/10 aislados

GenoType MTBDR plus INH
Resist
encia
en
katG
Resist
encia
en
inhA
Resist
encia
s no
det
ecta
das
0.00%
10.00%
20.00%
30.00%
40.00%
50.00%
47.36%
26.31% 26.33%
Sensibilidad a INH en 38 aislados MDR
18/38 aisla-dos 10/38
aisla-dos
0.00%10.00%20.00%30.00%40.00%50.00%
45.45%27.27% 27.28%
Sensibilidad a INH en 11 aislados no MDR
Resistencia de KatG + inhA=72.72
5/11 aislados 3/11
aislados
Resistencia de katG + inhA= 73.67
Fuente: Laboratorio de Microbiología Clínica, INER, 2014

GenoType MTBDR sl EMB
resistencia en emBB Resistencias no detectadas 0.00%
10.00%
20.00%
30.00%
40.00%
50.00%
60.00%
55.55%
44.45%
Resistencia a EMB en 11 aislados
5/9 aislados
4/9 aislados
Sensibilidad teórica para el gen embB 47%-65%
Fuente: Laboratorio de Microbiología Clínica, INER, 2014

GenoType MTBDR sl (FLQ Y AG)
0.00%20.00%40.00%60.00%80.00%
100.00%120.00%
0.00%
100.00%
Resistencia a FLQ en 3 aislados XDR
3/3 ais-lados
0/3 ais-lados
0.00%
20.00%
40.00%
60.00%66.66%
33.34%
Resistencia a AG en 3 aislados XDR
2/3 ais-lados
1/3 aislados